A internet ama gatos, então imagino que o Cloud vai me render mais visualizações do que todos os meus outros posts somados.
Quando minha esposa me presenteou com um kit de Sequenciamento de Genoma Completo da Basepaws para o nosso amado gato Cloud no Natal passado, fiquei bastante empolgado. Não só porque é fantástico que essa tecnologia exista e seja comercialmente viável, mas também porque, como bioinformata acostumado a analisar dados genômicos humanos, sei o quanto é desafiador descobrir e relatar achados realmente significativos a partir de um genoma comparativamente pouco estudado, como o de Felis catus.
Fiquei curioso para saber até onde essa empresa conseguiria fornecer informações interessantes ou acionáveis sobre o meu pet, e também o quanto eu mesmo conseguiria extrair de útil ao rodar análises nos dados brutos de sequenciamento. Não é uma tarefa simples — para concluir análises genômicas com bom custo-benefício, é preciso encadear muitas ferramentas complexas em um pipeline, e a execução de cada etapa precisa ser orquestrada para rodar em máquinas de tamanhos e capacidades variados. Quem sou eu para recusar um desafio desses em nome do meu bichano fofo?
Antes de falar sobre como usei a versão mais recente do Cloud Composer (o serviço totalmente gerenciado de Apache Airflow do GCP) para simplificar a execução automatizada e a visualização de várias etapas complexas de análise genômica, e como usei o Claude 3.5 Sonnet no AWS Bedrock para analisar os resultados, quero começar destacando o quanto fiquei impressionado com o relatório em PDF gerado pela Basepaws.
Com 68 páginas, ele tem muito mais conteúdo do que cabe neste artigo. Mas, em resumo, o relatório informa com clareza, sobre o seu pet:
- Dados de grupo de raça (uma amostra aparece abaixo)
- A presença/ausência de marcadores genéticos de saúde e de distúrbios genéticos
- Vários marcadores de traços interessantes
- E, para minha surpresa, um relatório de saúde bucal baseado no microbioma oral
O relatório de saúde bucal, em especial, foi bem legal: confirmou alguns problemas que eu já conhecia (por exemplo, risco "Médio" de doença periodontal) e mostrou que as ações para mitigar outros problemas têm dado certo (por exemplo, risco "Baixo" de reabsorção dentária, um problema provavelmente em parte de origem genética que ele tem há anos e que meus veterinários trataram com sucesso).
Já é bem difícil analisar o genoma de gato, que tem anotação relativamente pobre, mas também sequenciar o microbioma oral e entregar análises significativas e acionáveis em cima disso é uma conquista e tanto. Parabéns à equipe de cientistas que tornou isso possível.

Eu vinha pensando em adotar um Maine Coon como meu próximo gato — não imaginava que já tinha (mais ou menos) um!
Dito isso, vamos ver o que dá para fazer com os dados brutos de genoma completo que essa empresa entrega junto com o relatório.
O link abaixo leva a um repositório associado a este blog que usa a recém-lançada v3 do Cloud Composer e alguns outros serviços de ponta do GCP — todos provisionados com o Terraform fornecido — para ajudar você a automatizar, escalar e visualizar de ponta a ponta a execução da complexa teia de ferramentas necessárias para fazer análises secundárias e terciárias em dados de genoma completo de gato.
https://github.com/doit-mattporter/genomics-workflow-orchestration
Vamos começar entendendo, em linhas gerais, o que esse repositório vai executar para rodar análises genômicas de gatos no GCP.
Para quem não conhece bioinformática: de modo geral, há três grandes etapas de pipeline na análise de dados genômicos, independentemente do organismo. A análise primária já vem pronta quando você recebe os dados de sequenciamento da Basepaws, enquanto as análises secundária e terciária são executadas com a ajuda do código que disponibilizei. Essas três etapas estão descritas a seguir:
- Análise primária. Essa etapa acontece no laboratório de sequenciamento de DNA e envolve converter os dados brutos de sinal (dados de luz) das máquinas de sequenciamento em sequências de pares de bases de DNA (sequências de A/C/G/T). Também inclui verificações de QC, como remover chamadas de sequência de baixa confiança.
Por limitações técnicas, é impossível sequenciar uma fita de DNA do início ao fim em uma única leitura contínua. Em vez disso, as fitas precisam ser fragmentadas em milhões de pedaços curtos, que só então podem ser sequenciados. A saída da análise primária será, portanto, milhões — quando não bilhões — de fragmentos curtos de DNA, em geral com 100 a 300 pares de bases (bps) cada. Esses dados brutos e fragmentados de sequenciamento são entregues no formato FASTQ, basicamente um formato de texto simples com strings de pares de bases ACGT para essas milhões de sequências curtas. É isso que a BasePaws envia e o ponto de partida deste blog e do repositório associado. 2. Análise secundária. Essa etapa é como montar um quebra-cabeça gigante do seu DNA, em que a solução é sempre um pouco diferente da imagem da caixa. A análise secundária tem 2 grandes componentes:
a) "Alinhamento de Sequências", também conhecido como Montagem do Quebra-cabeça do DNA: aqueles milhões de fragmentos curtos de DNA da análise primária são reunidos novamente — com muito poder computacional — para reconstituir o genoma original e completo do gato de onde vieram.
b) "Variant Calling", ou Encontre as Diferenças: depois que o genoma do seu gato é remontado, ele precisa ser comparado com o genoma de "referência" que a comunidade científica definiu como padrão-ouro do que seria um genoma típico de gato. O seu gato vai se desviar desse padrão de "referência" pela sua singularidade genética; essa etapa procura justamente essas diferenças, os pontos em que o DNA do seu gato diverge do DNA "típico" de gato. Essas diferenças são chamadas de "variantes" ou "mutações". Nem toda mutação descoberta no variant calling é real — por motivos complicados, muitas são erros. Essa etapa também envolve QC, para garantir que as variantes sejam reais. 3. Análise terciária. Costuma ser a parte mais delicada e crucial: descobrir o que a lista única de diferenças de DNA encontrada na análise secundária realmente significa. A análise terciária é a apresentação de achados tangíveis e significativos. Algumas dessas variantes têm associação conhecida com condições de saúde? Como meu gato vai responder a diferentes opções de medicamentos com base nessa lista de mutações? Essa mutação específica é responsável pela cor do pelo dele? Esse conjunto de mutações sugere que meu gato tem ascendência Maine Coon? A análise terciária é a capacidade de responder a perguntas desse tipo.
Agora que você já tem uma boa noção do trabalho a ser feito, mãos à obra! Depois de receber os dados de genoma completo do seu gato pela BasePaws — ou se você só quiser acompanhar e ver o que dá para fazer com Cloud Composer e Claude usando esses dados — siga os passos abaixo.
O README do repositório descreve como começar provisionando a infraestrutura de nuvem necessária com um terraform apply. Atenção: alguns recursos, em especial o Cloud Composer, ficam ligados 24/7 até serem encerrados, então fique de olho nos seus gastos em nuvem e lembre-se de encerrar o que não estiver usando. Os principais recursos provisionados são:
Ambiente Google Composer
- Ambiente Composer 3 com Apache Airflow 2
- Configura uma DAG do Airflow para processar dados genômicos de gatos. Vale notar que essa DAG provisiona temporariamente instâncias c4-standard-96 e c4-standard-8 do Compute Engine, conforme exigido pelas várias etapas do pipeline.
Buckets do Google Cloud Storage
genomic_inputs,genomic_reference,genomic_outputsecloud_functionpara armazenar entradas (arquivos FASTQ), genomas de referência, saídas (VCFs e arquivos de anotação) e o código da Cloud Function
Google Cloud Function v2
- Função v2
genomic-dag-kickoffpara acionar a DAG de análise genômica - Acionada por evento de finalização de objeto no GCS. Essa função verifica se existe um arquivo
ready.txte, em seguida, usa a lista de localizações de bucket dos FASTQs contida nele para disparar a DAG e processar esses FASTQs.
Instância do Google Compute Engine
grabbing-reference-genomeé uma instância c4-standard-96 que baixa dois genomas de referência de gato no NCBI, indexa essas referências com o GATK e faz upload dos genomas processados para o bucketgenomic_reference, para uso posterior pela DAG.- Esse recurso só precisa rodar uma vez e se autoencerra assim que o trabalho termina.
Com esses recursos no ar a partir do terraform apply, basta fazer o seguinte para iniciar a análise genômica do gato:
- Faça upload dos FASTQs da BasePaws para o bucket
genomic_inputs_<random_id> - Crie um arquivo
ready.txtcom as URIs do GCS desses FASTQs e suba esse arquivo para o mesmo bucket.
O upload do ready.txt aciona a Cloud Function genomic-dag-kickoff. Essa função inicia a execução de duas instâncias da DAG no Cloud Composer, cada uma orquestrando a análise secundária e terciária contra uma das duas versões mais recentes do genoma do gato: Felis_catus_9.0 e Felis_catus_Fca126_mat1.0.
A DAG executa uma orquestração complexa de ferramentas de bioinformática que, no fim, nos entrega:
- Arquivos VCF, ou Variant Call Files. É uma lista de todas as mutações descobertas.
- Arquivos de anotação produzidos pelo SnpEff. O SnpEff fornece anotações in silico para cada mutação dentro de um gene codificador de proteína, com a probabilidade de que ela resulte em um impacto funcional "Baixo", "Moderado" ou "Alto" sobre a proteína codificada por aquele gene.
Em alto nível, a DAG é composta pelos seguintes Task Groups: os Task Groups de "alignment" e "variant calling" correspondem à Análise Secundária, e o Task Group de "annotation" representa a Análise Terciária:
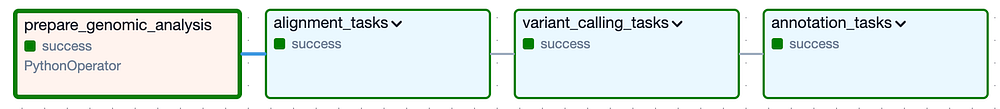
DAG do Cloud Composer para executar análise secundária e terciária em uma versão específica do genoma de gato
Ao expandir cada Task Group (mostrado abaixo), aparecem as muitas tarefas individuais necessárias para rodar esse pipeline de ferramentas e validar se os arquivos de saída esperados foram criados. Vale notar que incluí uma lógica para pular um Task Group inteiro se os arquivos de saída dele já estiverem no bucket de saída de uma execução bem-sucedida anterior.
Sem o Apache Airflow e a versão totalmente gerenciada dessa ferramenta open source no GCP, encadear essas ferramentas em pipeline e validar a execução bem-sucedida (ou já realizada anteriormente) de cada etapa seria muito mais difícil e demorado de implementar. Não só seria desafiador orquestrar essas etapas, como também recuperar e armazenar os logs, visualizar o progresso do pipeline em tempo real e reportar problemas.
O Composer facilita acompanhar o progresso, criar pipelines com caminhos lógicos ramificados e garantir que os erros sejam capturados e seus logs apresentados em uma UI fácil de interpretar. Por essas e outras razões — como a capacidade do Composer de escalar recursos de computação com bom custo-benefício em operações de porte empresarial — considero ferramentas de orquestração de workflows como o Composer essenciais para construir pipelines de dados escaláveis.
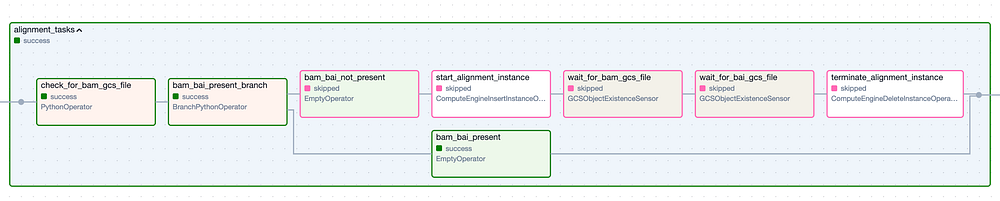
O Task Group "Alignment". Etapas com borda verde representam execuções bem-sucedidas; as com borda rosa foram puladas.
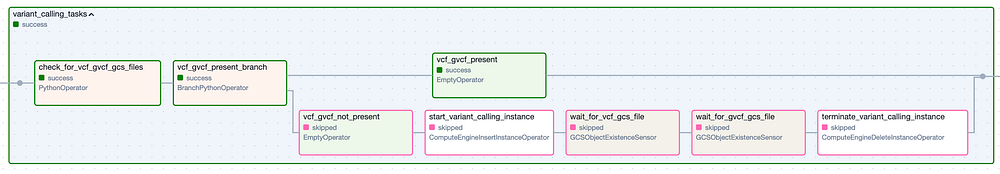
O Task Group "Variant Calling". Etapas com borda verde representam execuções bem-sucedidas; as com borda rosa foram puladas.
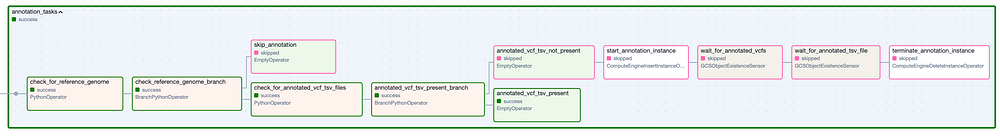
O Task Group "Annotation". Etapas com borda verde representam execuções bem-sucedidas; as com borda rosa foram puladas.
Quando tudo isso terminar de rodar, você verá os VCFs e os arquivos de anotação despejados no bucket GCS genomic-outputs-<random_id>. Os VCFs trazem a lista de todas as mutações descobertas, enquanto os arquivos de anotação detalham os efeitos previstos in silico pelo SnpEff dessas mutações sobre as proteínas codificadas pelos genes.
O nosso interesse aqui é especificamente em como o SnpEff acredita que os genes codificadores de proteína serão impactados.
Foi aí que minha admiração pelo serviço da BasePaws realmente começou a aparecer. Na genômica humana, há uma quantidade impressionante de fontes open source de anotação de variantes para se basear e obter um entendimento clínico profundo de praticamente qualquer mutação que ocorra dentro de um gene codificador de proteína. No mundo da genômica de gatos, em contraste, eu não encontrei nenhum banco de dados de anotação open source — nem mesmo um para mutações com desfechos clínicos claros e conhecidos. Como não tenho a menor vontade de raspar artigos acadêmicos para montar meu próprio banco, só me restou usar o SnpEff na etapa de anotação do pipeline da minha DAG no Cloud Composer, o que ao menos nos dá previsões in silico de efeito funcional para trabalhar. A BasePaws certamente investiu muito esforço em construir bancos de dados de anotação internos para conseguir oferecer o tipo de análise que vi no relatório que recebi.
Pois bem, determinado a tirar algum proveito das previsões de efeito do SnpEff, recorri a LLMs — mais especificamente, ao Claude 3.5 Sonnet rodando no AWS Bedrock.
Comecei executando os comandos bash a seguir no arquivo de anotação que o SnpEff produz. Esses comandos simples filtram os 13,5 milhões de mutações anotadas para apenas 366 com mais chances de serem "interessantes" — aquelas que:
- Estão dentro de uma região codificadora de proteína
- Têm mais chance de serem variantes legítimas, e não chamadas equivocadas
- Têm um homólogo humano identificado (uma LLM tem mais chance de entender o impacto potencial se conhecer a proteína humana equivalente), e
- Têm impacto previsto "HIGH" sobre o efeito funcional de uma proteína
head -n1 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff.ann.tsv > 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff_HIGH_impact.ann.tsv
grep "\tHIGH\t.*protein_coding" 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff.ann.tsv >> 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff_HIGH_impact.ann.tsv
grep -v "frameshift" 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff_HIGH_impact.ann.tsv |
grep -v "intron" |
awk '$11 !~ /^ENSFCAG000/' > 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff_HIGH_impact_filtered.ann.tsv
cut -f 1,2,4,5,8-11,17,18,19,21 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff_HIGH_impact_filtered.ann.tsv
Colei o conteúdo desse arquivo filtrado, com 366 variantes anotadas de impacto "HIGH", no Claude, junto com o seguinte prompt:
Analise as anotações genéticas do SnpEff a seguir para Felis catus 9.0. Ao mencionar um gene, indique quantas mutações foram descobertas naquele gene e não invente mutações para genes que não estão no arquivo de anotação colado abaixo. Por favor, forneça:
1. Um resumo dos achados mais significativos
2. Destaque mutações em genes associados a condições de saúde conhecidas, traços fenotípicos ou processos biológicos importantes.
3. Explique as implicações funcionais potenciais das 5 a 10 mutações mais interessantes, considerando a função do gene e o tipo de mutação.
4. Identifique padrões, agrupamentos de mutações ou vias biológicas/funcionais impactadas que mereçam atenção.
5. Sugira possíveis preocupações de saúde ou traços que possam ser afetados com base nessas mutações, mas deixe claro que isso é especulativo sem correlação clínica.
Use terminologia científica quando apropriado, mas também forneça explicações em linguagem acessível para garantir o entendimento. Se precisar de qualquer esclarecimento ou informação adicional sobre o fenótipo ou histórico de saúde do sujeito para melhorar a análise, é só perguntar.
O gato tem pelagem totalmente branca, 11 anos e nenhum problema de saúde conhecido além de reabsorção dentária felina. Ele não tem deficiências neurológicas ou do sistema imunológico conhecidas (fora a possível ligação entre função imunológica e reabsorção dentária felina).
O resultado foi o que segue, e achei bem interessante, já que o Claude sugere uma possível predisposição genética à reabsorção dentária felina com base em alguns dos genes com mutações de alto impacto. Com a pelagem totalmente branca, é bom estar ciente da possibilidade de ele também ter risco maior de câncer, caso a funcionalidade de uma proteína de reparo de DNA esteja comprometida — isso reforça que devo limitar o tempo de exposição dele à luz solar direta.
Já os outros achados do Claude são bastante especulativos, porque eu não observei nenhum dos problemas sérios de função muscular ou metabolismo relatados. Como não há conjuntos de dados de anotação publicamente disponíveis e bem organizados, a função dos genes de gato é, em grande parte, inferida via homologia com os genes humanos equivalentes. Por isso, espero que as LLMs respondam com inferências amplas e centradas em humanos, levando aos resultados excessivamente especulativos que o Claude produziu.
Obrigado por fornecer essas informações genéticas detalhadas sobre seu gato branco de 11 anos com reabsorção dentária felina. Vou analisar as mutações de alto impacto com base nas anotações do SnpEff que você compartilhou. Vamos dividir isso nas seções solicitadas:
1. Resumo dos Achados Mais Significativos:
Os dados genéticos revelam um número substancial de mutações de alto impacto em vários genes. Essas mutações incluem variantes do tipo stop-gained, start-lost e stop-lost, que podem alterar significativamente a função das proteínas. No total, há mais de 200 mutações de alto impacto identificadas em diversos genes.
2. Mutações em Genes Associados a Condições ou Traços Conhecidos:
a) LRRC45 (1 mutação): associado à função ciliar, que pode afetar vários processos fisiológicos.
b) PNKP (1 mutação): envolvido no reparo do DNA, com potencial impacto na suscetibilidade ao câncer e na função neurológica.
c) ATP2A1 (1 mutação): crítico para a função muscular, especialmente em fibras musculares de contração rápida.
d) COQ7 (1 mutação): importante para a biossíntese de coenzima Q10, afetando a produção de energia nas células.
e) ABCC6 (1 mutação): associado a distúrbios de tecido conjuntivo em humanos.
f) CRP (1 mutação): envolvido na resposta imunológica e na inflamação.
3. Implicações Funcionais Potenciais das Principais Mutações:
a) PNKP (c.1150C>T, p.Gln384*): essa mutação stop-gained pode levar a uma proteína truncada, prejudicando potencialmente os mecanismos de reparo do DNA. Isso pode aumentar a suscetibilidade a danos no DNA e, teoricamente, afetar a função neurológica ou o risco de câncer.
b) ATP2A1 (c.3149A>G, p.Ter1050Trpext*?): essa mutação stop-lost pode resultar em uma proteína estendida. ATP2A1 é crucial para a contração muscular, e alterações poderiam afetar a função muscular.
c) COQ7 (c.817T>A, p.Ter273Lysext*?): outra mutação stop-lost, que também pode levar a uma proteína estendida. COQ7 é vital para a produção de coenzima Q10, essencial para a produção de energia celular. Alterações podem afetar o metabolismo energético geral.
d) ABCC6 (c.4246C>T, p.Arg1416*): essa mutação stop-gained pode resultar em uma proteína truncada. Em humanos, mutações em ABCC6 estão associadas ao pseudoxantoma elástico, uma condição que afeta o tecido conjuntivo.
e) CRP (c.592T>C, p.Ter198Glnext*?): essa mutação stop-lost no gene da proteína C-reativa pode afetar respostas inflamatórias e a função imunológica.
4. Padrões e Observações Dignas de Nota:
Parece haver um agrupamento de mutações afetando genes envolvidos na função muscular, no metabolismo energético e na resposta imunológica. Várias mutações são encontradas em genes ligados ao reparo do DNA e a processos de manutenção celular.
5. Possíveis Preocupações de Saúde ou Traços (Especulativo):
Com base nessas mutações, podem existir preocupações potenciais relacionadas a:
\* Função muscular e metabolismo (ATP2A1, COQ7)
\* Regulação do sistema imunológico (CRP)
\* Reparo do DNA e potencial suscetibilidade ao câncer (PNKP)
\* Saúde do tecido conjuntivo (ABCC6)
No entanto, é fundamental enfatizar que a presença dessas mutações não significa necessariamente que o gato vai desenvolver as condições relacionadas. Muitos fatores, incluindo influências ambientais e outros modificadores genéticos, têm papel na expressão gênica e no desenvolvimento de doenças.
É interessante notar que, apesar dessas mutações, seu gato chegou aos 11 anos sem problemas de saúde importantes relatados, fora a reabsorção dentária felina. Isso reforça a relação complexa entre genótipo e fenótipo.
Dado o histórico de reabsorção dentária felina do gato, as mutações em genes ligados à função imunológica (como CRP) e ao tecido conjuntivo (como ABCC6) podem ser de interesse particular, já que se acredita que esses sistemas tenham papel nessa condição. Ainda assim, uma ligação direta só pode ser estabelecida com mais pesquisas.
Em seguida, decidi investigar quais genes são conhecidos por estar associados à pelagem branca em gatos e, então, filtrar todas as mutações anotadas pelo SnpEff dentro desses genes, independentemente da previsão de impacto baixo/médio/alto. Isso foi feito filtrando o arquivo de anotação por mutações nos genes KIT e KITLG:
head -n1 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff.ann.tsv > 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff_LOW_MODERATE_impact_white_coat.ann.tsv
grep -E "\t(LOW|MODERATE)\t.*protein_coding" 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff.ann.tsv | grep -E '\tKIT\t|\tKITLG\t' >> 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff_LOW_MODERATE_impact_white_coat.ann.tsv
cut -f 1,2,4,5,8-11,17,18,19,21 31220812113030_GCF_000181335.3_Felis_catus_9.0_genomic_snpeff_LOW_MODERATE_impact_white_coat.ann.tsv
Reaproveitando o mesmo prompt, o Claude conjectura que as mutações missense e em sítios de splice de íntron são provavelmente responsáveis pela pelagem branca do Cloud:
Obrigado por fornecer as anotações genéticas para Felis catus 9.0. Vou analisar esses dados e fornecer as informações solicitadas. Vamos detalhar os achados:
1. Resumo dos achados mais significativos:
As anotações revelam múltiplas mutações em dois genes importantes: KIT e KITLG. Esses genes fazem parte da via de sinalização KIT/KITLG, que tem papéis cruciais em vários processos biológicos, incluindo o desenvolvimento da cor da pelagem, hematopoiese e gametogênese.
Gene KIT: 9 mutações (7 variantes sinônimas, 2 variantes em região de splice)
Gene KITLG: 2 mutações (1 variante missense, 1 variante sinônima)
O achado mais significativo é a variante missense no gene KITLG, que pode afetar a função da proteína.
2. Mutações associadas a condições de saúde conhecidas, traços fenotípicos ou processos biológicos importantes:
Os genes KIT e KITLG estão associados à cor da pelagem em gatos, em especial a padrões de manchas brancas. A pelagem totalmente branca deste gato pode estar relacionada a essas mutações, especialmente considerando o número de variantes no gene KIT.
3. Implicações funcionais potenciais das 5 a 10 mutações mais interessantes:
a) Variante missense em KITLG (c.731G>A, p.Ser244Asn): essa mutação altera uma serina por uma asparagina na posição 244 da proteína KITLG. Como muda a sequência de aminoácidos, pode afetar a função da proteína. KITLG é crucial para a sobrevivência e proliferação de melanócitos, que produzem pigmento. Essa mutação pode contribuir para a pelagem totalmente branca do gato.
b) Variantes em região de splice em KIT (c.2491–3C>T, c.1353–5T>C, c.1122–4_1122–3delGT): essas mutações ocorrem em regiões de splice, importantes para o processamento adequado do mRNA. Embora classificadas como de baixo impacto, podem afetar o splicing do gene KIT, levando a alterações na produção ou função da proteína. A proteína KIT é uma tirosina quinase receptora envolvida em vários processos de desenvolvimento, incluindo o de melanócitos.
c) Variantes sinônimas em KIT: embora as variantes sinônimas não alterem a sequência de aminoácidos, ainda podem impactar a expressão gênica por vários mecanismos, como mudanças na estabilidade do mRNA ou na eficiência de tradução. O alto número de variantes sinônimas no gene KIT (7 no total) pode, em conjunto, influenciar sua expressão ou função.
4. Padrões, agrupamentos de mutações ou vias biológicas impactadas:
As mutações estão concentradas na via de sinalização KIT/KITLG, crucial para o desenvolvimento e a função dos melanócitos. Essa via também está envolvida na hematopoiese (formação de células sanguíneas) e na gametogênese (produção de células reprodutivas). A concentração de mutações nesses genes sugere um possível impacto na pigmentação e talvez em outros processos relacionados.
5. Possíveis preocupações de saúde ou traços que podem ser afetados (especulativo):
a) Cor da pelagem: a pelagem totalmente branca do gato provavelmente está relacionada a essas mutações, em especial nos genes KIT e KITLG.
b) Audição: alguns gatos totalmente brancos com mutações em KIT são propensos a surdez congênita. Embora nenhuma mutação específica associada à surdez esteja presente aqui, pode valer a pena monitorar a audição do gato.
c) Função imunológica: a via KIT/KITLG tem papel na hematopoiese, incluindo o desenvolvimento de certas células imunológicas. Embora o gato não tenha deficiências conhecidas do sistema imunológico, essas mutações podem influenciar a função imunológica de forma sutil.
d) Reabsorção dentária: embora não esteja diretamente ligada a KIT/KITLG na literatura atual, o envolvimento da via em vários processos de desenvolvimento pode contribuir indiretamente para problemas dentários. Isso é altamente especulativo e exigiria mais pesquisas para estabelecer qualquer conexão potencial.
e) Fertilidade: dado o papel de KIT/KITLG na gametogênese, podem haver efeitos potenciais sobre a fertilidade. No entanto, isso é especulativo e só seria relevante caso o gato fosse usado para reprodução.
É importante notar que, embora esses achados genéticos sejam interessantes, sua significância clínica só pode ser determinada por correlação com o estado de saúde real do gato e com mais estudos. A boa saúde atual do gato aos 11 anos sugere que muitas dessas mutações podem não ter impactos graves.
O que tiro disso tudo é que dá para extrair achados bem interessantes dos dados genômicos do seu gato, e obter esses dados se torna muito mais viável, confiável e escalável com a ajuda de serviços de nuvem que orquestram pipelines de dados, como o Cloud Composer.
Mas ainda há muito a fazer do lado da pesquisa pública. Inferir a funcionalidade de genes de gato a partir da homologia com genes humanos só permite análises significativas até certo ponto. Quando as instituições de pesquisa veterinária começarem a publicar bancos de dados de anotação genômica para gatos e cães, acredito que vamos começar a ver as análises de dados genômicos com LLMs realmente brilharem. Até lá, fico impressionado com o trabalho científico que a equipe da Basepaws tem feito.
E é isso! Percorremos a fascinante fronteira da genômica felina, do impressionante relatório da BasePaws à nossa análise caseira impulsionada por serviços de computação em nuvem de ponta e IA generativa. E embora orquestrar uma sinfonia de ferramentas genômicas possa ser tão complicado quanto reunir gatos, serviços como o Cloud Composer tornam tudo bem mais fácil.